Feuerbrand bekämpfen und Salmonellen nachweisen
ETH-Forscher schufen eine wirksame Waffe gegen die Pflanzenkrankheit Feuerbrand und eine neue Nachweismethode gegen Salmonellen. Beide fussen auf besonderen Viren, die spezifisch nur eine Bakterienart befallen.

Die Pflanzenkrankheit Feuerbrand, ausgelöst durch das Bakterium Erwinia amylovora, ist bei Obstbauern gefürchtet. Das Bakterium befällt Apfel- und Birnbäume und andere Rosengewächse. Ist ein Baum befallen, muss er meist gefällt und restlos verbrannt werden.
Die Bekämpfung des Feuerbrand-Erregers ist schwierig. In Ausnahmefällen dürfen Bauern das Antibiotikum Streptomycin einsetzen. Doch auch dieses kann nicht verhindern, dass sich der Erreger etwa über bestäubende Insekten weiterverbreitet.
Den Feind des Feindes nutzen
Eine neue Bekämpfungsstrategie präsentieren nun Forschende um ETH-Professor Martin Loessner: Sie statteten ein Bakterienvirus (in der Fachsprache Bakteriophage genannt) mit der Bezeichnung Y2, das ausschliesslich den Feuerbrand-Erreger befällt, mit zusätzlichen Genen aus. Damit schufen sie eine hochwirksame und hochspezifische Waffe gegen dieses Bakterium.
Bereits die Naturform von Y2 ist eine geborene Erwinia-Killerin, allerdings kann dieser Bakteriophage die zähe Schleimhülle, mit der sich das Bakterium schützt, nicht genügend gut durchdringen. Der Bakterienschleim ist äusserst zäh und verstopft die Leitgefässe von Pflanzen, so dass Blüten und Blätter verdorren.
Anders ein zweiter Erwinia befallender Bakteriophage, L1. Dieser kann dank speziellen Enzymen den Schleim effizient auflösen. L1 vermag aber den Feuerbrand-Erreger nicht so effektiv abzutöten.
Y2 mit schleimlösenden Fähigkeiten ausstatten
Indem die Forschenden das Gen für dieses Enzym von L1 in den Y2-Phagen einbauten, schufen sie eine genetische veränderte Variante, die beides kann: Sie ist für das Erwinia-Bakterium hochinfektiös und absolut tödlich und kann effizient dessen Schleimhülle auflösen.

Sobald Y2 in das Bakterium gelangt, beginnt es sich massenhaft zu vermehren. Anschliessend löst dieser Virus das Bakterium von Innen auf um freizukommen und um weitere Bakterien befallen zu können. Dabei gelangen auch schleimauflösende Enzyme in rauen Mengen in die Umgebung. Dies beschleunigt den Abbau der Schleimhülle von weiteren Bakterien und erleichtert dadurch deren Infektion. Die Vernichtung schreitet so rasch voran.
«Unser Bakteriophage erwies sich als sehr wirksam gegen den Feuerbrand-Erreger, nicht nur im Labor, sondern auch bei infizierten Apfelblüten», sagt Loessner. Die Tests wurden mit verseuchtem Pflanzenmaterial in Gewächshäusern mit den höchsten Sicherheitsstandards durchgeführt. Feldversuche gab es bisher jedoch nicht: «Feuerbrand ist eine der schlimmsten Pflanzenkrankheiten, da kann man nicht im Feld experimentieren», betont der ETH-Professor.
Aus Virus wird Sensor
Die Forscher schufen jedoch nicht nur Bakterienkiller. Mithilfe eines anderen Gens erzeugten sie eine zweite Y2-Variante, mit welcher sie den Feuerbrand-Erreger nachweisen können. Das Gen sorgt dafür, dass die Bakterien anfangen zu leuchten, wenn sie von den Bakteriophagen befallen werden. Dieses Licht lässt sich einfach messen und für den gezielten Nachweis des Erregers nutzen.
Diese Methode ist nicht nur schnell und sehr zuverlässig, sie ist auch äusserst empfindlich: «Mit Hilfe unserer Sensor-Phagen reichen schon wenige tausend infizierte Bakterien aus, um Feuerbrand nachweisen zu können», betont Loessner. Bisherige Nachweismethoden seien viel langsamer, weniger empfindlich und lägen gelegentlich auch falsch. Weil der Y2-Sensor-Phage jedoch nur Erwinia infiziere, könne es keine falschen Diagnosen geben, so der Forscher.
Spezifität als Grundlage für Salmonellen-Nachweis
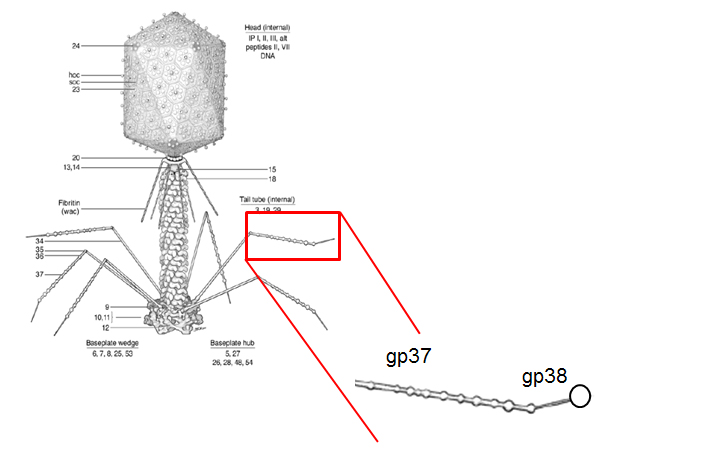
Die Tatsache, dass Bakteriophagen generell sehr wirtsspezifisch sind, machten sich Loessner und seine Mitarbeiter auch auf andere Weise zunutze: für den Nachweis von Salmonellen. In einer zweiten Publikation, die ebenfalls in der Fachzeitschrift Applied and Environmental Microbiology erschien, zeigen die ETH-Forschenden auf, wie sie mithilfe von synthetisch hergestellten Einzelteilen von Bakteriophagen eine universelle Nachweismethode für Salmonellen entwickelten. Damit lassen sich sämtliche 2500 bekannten Unterarten (Subtypen) aufspüren. Bisherige Methoden auf der Basis von Antikörpern erkennen immer nur einen Teil dieser Unterarten und sind zudem langsamer.
Loessners Team hat dazu einen bestimmten Bestandteil des salmonellenspezifischen Bakteriophagen S16 nachgebaut. An diesem Teil, einer Viren-Schwanzfaser, befindet sich auch ein kugeliges Bindeprotein, das an zwei bestimmte Oberflächenstrukturen aller Salmonellen-Subtypen anhaften kann. Die künstliche Schwanzfaser mitsamt der Erkennungsstruktur wiederum werden auf der Oberfläche von mikroskopisch kleinen magnetischen Kügelchen befestigt.
Damit lassen sich nun fast beliebige Flüssigkeiten und Proben auf die Anwesenheit und Menge von Salmonellen testen. Sobald die Salmonellen an die Fasern auf den Magnetkügelchen binden, bildet sich im Testgefäss eine Art rostiges Aggregat, welches sich leicht mit einem externen Magneten abtrennen lässt.
Literaturhinweis
Born Y, et al. Engineering of Bacteriophages Y2::dpoL1-C and Y2::luxAB for Efficient Control and Rapid Detection oft the Fire Blight Pathogen, Erwinia amylovora. Applied and Environmental Microbiology. June 2017 Volume 83 Issue 12 e00341-17. DOI: externe Seite10.1128/AEM.00341-17call_made
Denyes JM, et al Modified Bacteriophage S16 Long Tail Fiber Proteins for Rapid Specific Immobilization and Detection of Salmonella Cells. Applied and Environmental Microbiology. June 2017 Volume 83 Issue 12 e00277-17. DOI: externe Seite10.1128/AEM.00277-17call_made
